プレスリリース
国立研究開発法人海洋研究開発機構
メタゲノムを機能的に解析する最新版「MAPLEシステム」の公開
~環境からヒト腸内細菌叢までを高速に、簡単に~
1. 概要
国立研究開発法人海洋研究開発機構 (理事長 平朝彦) 海底資源研究開発センターの髙見英人上席研究員らが開発した、生物のゲノム、環境やヒト糞便サンプルなどの微生物叢の網羅的ゲノム (メタゲノム)に潜む生理・代謝機能を自動的に解析する「生理・代謝機能ポテンシャル評価システム(Metabolic and Physiological Potential Evaluator。以下「MAPLEシステム」という、図1)」を最新のスーパーコンピュータ(Data analyzer システム)に搭載し、従来の10〜15倍の高速化を実現する改良を施した最新版MAPLE ver. 2.3.1(図2)を9月26日から利用公開します。
高速化されたMAPLEシステムの最新版は、専門知識がなくても誰でも利用可能となり、解析容量を従来の3倍の300万配列まで増加することでより詳細な解析を実現しました。また、MAPLEシステムの計算結果を分かりやすく可視化するためのソフトウェアを2種類開発し、全ての利用者が自由に使えるダウンロードサイトもMAPLEシステム上に設置しました。これらのソフトは利用者のパソコン(MacやWindows)で簡単に使うことができます。さらに、海洋研究開発機構のスーパーコンピュータには、MAPLEシステムに対する最適化設計、高速ジョブスケジューラの開発や柔軟かつ堅牢なシステム基盤の構築を行っており、安全で安定した高速利用環境の提供を可能としています。
本成果は、基礎研究のみならずメタゲノム解析に基づく環境影響評価やヒト腸内細菌叢機能評価など応用研究の更なる進展に貢献すると期待されます。また、MAPLEシステムは海洋研究開発機構のスーパーコンピュータ以外の一般のサーバにも搭載可能であり、今後、民間企業等による積極的な活用も期待されることから、更なる利便性の向上とともにシステムの提供についても検討中です。
2.MAPLEシステム開発経緯
様々な環境に生息する微生物叢のゲノムをまるごと解析するメタゲノム解析(※1)は、微生物叢を構成する「だれが」「どのぐらいの割合で存在し」「どんな機能を」「どのぐらいもっているか」を知ることを目的として行われています。しかし、実際には、主に16S rRNA 遺伝子(種の同定に用いられる遺伝子)のPCR反応(※2)による増幅産物に基づく菌叢解析や特定の機能に関与する一部の鍵遺伝子の多様性解析が行われてきたにすぎません。
これは、メタゲノム配列から詳細な生理・代謝機能を簡便に調べる術がなく、微生物叢が有する網羅的機能のポテンシャル解析が困難だったからです。しかし、ゲノム中の16S rRNA 遺伝子のコピー数(※3)は生物種によって大きく異なることや、PCR 反応による遺伝子増幅に必要なプライマー(短い塩基配列)設計にも限界があるため、環境の微生物叢組成や潜在的機能の実態をどこまで正確に捉えているかは、更なる議論の余地があると考えられていました。
この問題解決のため、16S rRNA 遺伝子や一部の機能遺伝子のみを対象とした解析ではなく、複数の遺伝子の連続的作用によってなし得る生理・代謝機能を網羅的に解析することを可能としたMAPLEシステムが開発されました。MAPLEシステムは、髙見英人上席研究員が考案し、京都大学化学研究所の五斗進准教授(現ライフサイエンス統合データベースセンター(DBCLS)教授)らの協力を得て、2013年にゲノムネット(https://www.genome.jp/en/)から公開されました。一方、公開当初は10万配列が限界だったメタゲノム配列も、近年のゲノム配列決定の飛躍的技術革新によって大量の配列データが安価に得られるようになり、メタゲノム解析にも数100万配列が用いられるようになってきました。
その反面、複数サンプル間の比較によって微生物叢組成や機能的違いをハイライトするMAPLEシステムの利用者にとっては、膨大な計算時間が研究のネックとなってきました。このような背景から、従来よりも大量のデータを高速に処理するMAPLEシステムの開発が求められていました。
3.MAPLEシステムでわかること
MAPLEシステムでわかることは、大きく以下の4点です。
- (1)
- Kyoto Encyclopedia of Genes and Genomeデータベース(以下「KEGGデータベース」という、※4)に登録された機能モジュールに基づく生理・代謝機能の有無
- (2)
- 各生理・代謝機能の豊富さ
- (3)
- どんな生物種がどのぐらい各機能を担っているか(機能を担う生物種の割合)
- (4)
- リボソームタンパクに基づく微生物叢を構成する生物種の割合
KEGGデータベースには、生命活動の礎となる生理・代謝機能反応を複雑な代謝経路から反応単位(解糖系、TCAサイクル、アミノ酸合成など)で切り出し、小さな経路として定義した約770種類の機能モジュールが登録されています。
MAPLEシステムは、これらの機能モジュールが環境メタゲノム中の遺伝子によってどの程度充足されるかを自動的に計算することで、各環境中の微生物叢が有する潜在的生理・代謝機能とその豊富さを評価することを可能とした世界的にも例のないユニークなシステムです。
また、リボソーム(※5)を構成するタンパク質を評価基準に用いるMAPLEシステムは、16S rRNA 遺伝子を用いた際に生じる問題を解決し、より正しい評価基準でメタゲノムを構成する菌叢組成の解析も可能となりました。
4.最新版MAPLEシステムの特長
(1)解析対象となる生物、環境微生物叢の幅広さ
MAPLEシステムはゲノムが完成した生物であればどんな生物でも、また微生物が生息する環境であれば、海洋、陸地、極域環境のメタゲノムやヒト腸内細菌叢や口腔内、皮膚などに生息する常在菌叢の組成や生理代謝機能を解析することができます。
(2)高速化した計算時間
従来のMAPLEシステムでは、100万配列の計算に約2日を要していましたが、MAPLE ver. 2.3.1では5〜6時間、またこれまで解析できなかった300万配列では、10〜15時間で解析が終了します。
解析に用いられるゲノムデータベースは、KEGGデータベースに登録されている完成ゲノムから1種1ゲノムを選択した3622ゲノム(原核生物3186、真核生物436:平成30年7月13日現在)で年に1回のペースでデータベースが更新されます。
(3)簡単に可視化可能なソフトウェア
MAPLEシステムによる計算結果を簡単に可視化する2つのソフトウェアを新たに公開しました。
1)MAPLE Graph Maker (エクセル形式でダウンロードできるMAPLEの計算結果ファイルを読み込むことで簡単に結果を棒グラフ化することができるソフト:Mac、Windowsのパソコンで利用可)
2)MAPLE Metabolic Map Viewer (エクセル形式でダウンロードできるMAPLEの計算結果ファイルを読み込むことで簡単に生理・代謝機能を代謝マップとして描画できるソフト(図3):Mac、Windowsのパソコンで利用可)
【用語説明】
※1 メタゲノム解析:環境中に生息する微生物のほとんどが難培養性であることから、微生物の分離・培養という手法を経ずに微生物集団から直接抽出したゲノムDNAを網羅的に解析する方法
※2 PCR反応:ゲノムから特定の遺伝子をDNAポリメラーゼという酵素を使って増幅する方法で、増幅する遺伝子の両端の塩基位配列の一部 (プライマー) を2本鎖DNAのそれぞれの1本鎖に付着させ、プライマー間の遺伝子領域が増幅される。
※3 コピー数:生物のゲノム中には進化の過程でゲノム内に元は一つだった遺伝子が複製の過程で、同じ機能を持つ複数の遺伝子が作られる場合がある。この複数の遺伝子の存在度をコピー数という言葉で表現している。つまり、同じ機能の遺伝子が3つゲノム中にある場合は、コピー数3と表現する。コピー数が3つの遺伝子をPCRで増幅する場合、コピー数が1の場合と比べ3倍増幅されることになる。
※4 KEGGデータベース:Kyoto Encyclopedia of Genes and Genomeの略で、京都大学 化学研究所で開発されたゲノム、代謝機能データベース。ゲノム配列が完成した全ての生物種のゲノム配列情報と、各生物種が持つ代謝マップがデータベース化されている。世界的に最もよく用いられている代謝データベースの一つ
※5 リボソーム:全生物に共通に存在し、生体内でタンパク質を合成する工場にあたる巨大機能分子で、バクテリアは52、古細菌は58、真核生物は77のリボソームタンパク質で構成されている。基本的にゲノム中に各遺伝子が1つずつ(1コピー)しか存在しない。MAPLEではこの特徴を利用して、環境中の生物種組成が計算されている。
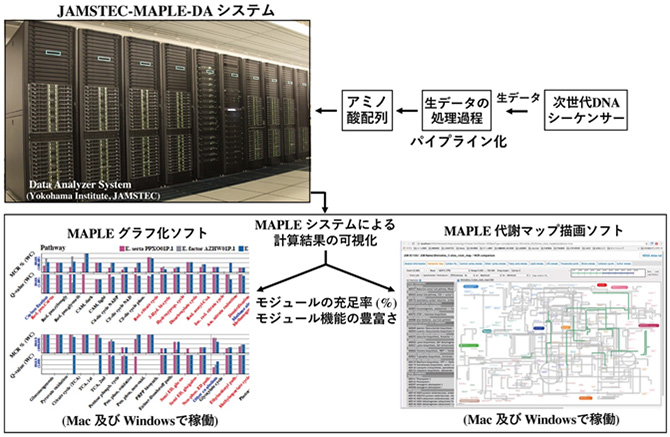
図1. MAPLEシステムの概要

図2. MAPLEシステムの初期画面
(URL: https://maple.jamstec.go.jp/maple/maple-2.3.1/)
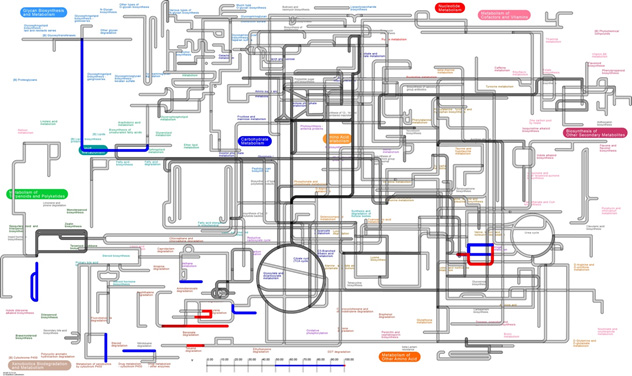
図3.生理・代謝機能を代謝マップとして描画できるソフト(MAPLE Metabolic Map Viewer)のイメージ
- 国立研究開発法人海洋研究開発機構
- (MAPLEシステムについて)
- 海底資源研究開発センター 環境影響評価グループ 上席研究員
髙見 英人 - (報道担当)
- 広報部 報道課長 野口 剛